MATÍAS ARIEL CABALLERO
REPLICACIÓN Y TRANSCRIPCIÓN
El genoma de individuo está contenido en las moléculas ADN de sus cromosomas y
mitocondrias. En ellas se encuentran las unidades de información llamadas genes.
Genes: son porciones de ADN que dirigen la síntesis de las distintas especies de ARN.
En cada división celular, el ADN de la célula madre pasa a las células hijas, ello exige
la duplicación o replicación del ADN original. La información que el ADN contiene debe
ser transferida a moléculas de ARN por un proceso denominado transcripción. La
síntesis de cadenas polipeptídicas requiere la traducción del mensaje cifrado en el
ARNm.
REPLICACIÓN DE ADN
Todas las células somáticas del organismo, originadas por divisiones sucesivas de la
célula huevo, poseen igual cantidad de ADN, con la misma estructura primaria. Esto
revela la capacidad de transmitir la información contenida en el ADN nuclear.
Replicación de ADN es semiconservadora
Cada una de las cadenas de ADN de la célula madre sirve de molde o guía para la síntesis
de una nueva hebra polinucleótida complementaria; de esta manera se forman 2 dobles
hélices idénticas a la original. Esto se llama replicación del ADN.
En el ADN una hebra es nueva y la otra procede de la progenitora, por eso se dice que es
semiconservadora. La replicación de ADN tiene lugar antes de la mitosis, durante la fase
S del ciclo celular.
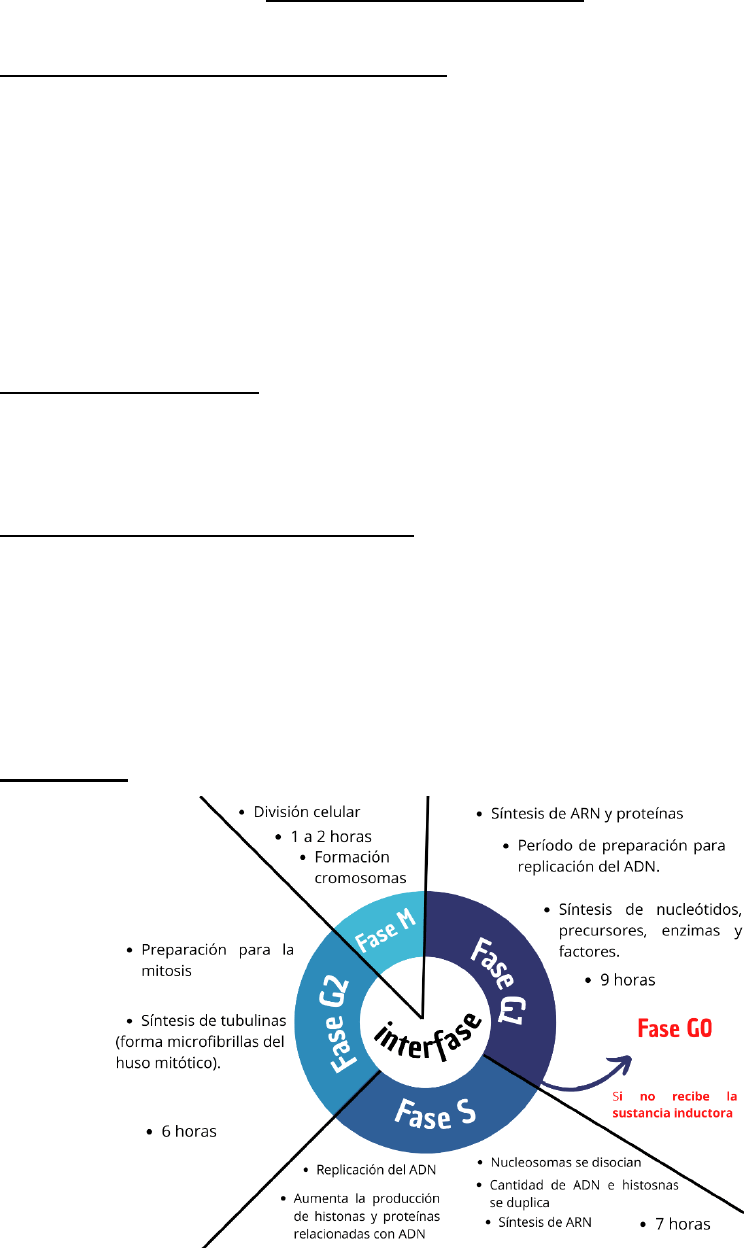
Ciclo celular
Las fases de G1 y G2 son muy breves en células con gran actividad mitótica. Otras células
pueden permanecer mucho tiempo sin multiplicarse.
El Ciclo celular es regulado por un complejo de proteínas, ciclinas y quinasas
dependientes de ciclinas, activadas por agentes externos que se unen a receptores
específicos en la MP y transmiten señales al interior de la célula.
MATÍAS ARIEL CABALLERO
Si no llegan señales activadoras, se mantienen en un estado no proliferativo, denominado
G0, en el que se cumplen todas las funciones metabólicas pero la célula no se divide.
Alteraciones en el proceso de regulación del ciclo celular pueden incrementar la actividad
mitótica y generar tumores malignos.
Enzimas y factores que intervienen en el proceso de replicación
Paso inicial de la replicación: separación de las 2 cadenas
Sitio de origen o iniciación: secuencias específicas de bases que sirven de reconocimiento
para el complejo de enzimas y factores que inicia la replicación. Generalmente contiene
secuencias ricas en pares A-T.
El primer paso es la formación del complejo de reconocimiento del origen (ORC),
formado por 6 subunidades. Luego se agrega el complejo de mantenimiento del
minicromosoma (MCM), también de 6 subunidades.
Los cromosomas de procariotas, ADN mitocondrial y ADN virales circulares tienen un
solo sitio de origen. En cambio, las enormes moléculas lineales empiezan en múltiples
sitios.
La separación se inicia en todos los cromosomas y en muchos puntos de la molécula de
ADN de cada uno de ellos. Así se producen “burbujas” en la zona de replicación, llamados
replicones. El desenrollamiento se completa con mayor rapidez que si se efectuara
progresivamente de un extremo a otro.
El sitio en el cual las 2 cadenas se separan es denominado horquilla de replicación, en
cada burbuja se producen 2 horquillas que avanzan en sentidos opuestos alejándose del
punto de origen.
Helicasa
Cataliza la separación de las cadenas de ADN. Requiere energía provista por la hidrólisis
de ATP.
Topoisomerasas
Las moléculas lineales de cromosomas de eucariotas, por su longitud y múltiples
interacciones en los agrupamientos de nucleosomas, carecen de libertad para rotar; por
ello se producen torsiones por delante de las horquillas de separación. El problema se
resuelve efectuando cortes transitorios de la cadena en las zonas hipertensionadas. Estos
cortes son catalizados por Topoisomerasas.
Topoisomerasa I: corta una de las hebras de la doble hélice y alivia la tensión por rotación
libre de la cadena seccionada sobre la otra. NO requiere energía.
Topoisomerasa II o girasa: secciona las 2 hebras de ADN. Es dependiente de ATP.
Ambas enzimas tienen capacidad para unir los cabos de las cadenas cortadas y
reestablecer la continuidad de la doble hélice una vez alcanzado el estado relajado.
Proteínas que mantienen las hebras separadas
A medida que las hebras de doble hélice se separan se unen a ellas proteínas fijadoras de
ADN monocatenario; las de las bacterias son designadas SSB y las de eucariotas

MATÍAS ARIEL CABALLERO
proteínas A de replicación (RPA). Estas proteínas estabilizan las monohebras e impiden
su reasociación.
Helicasas y proteínas de fijación avanzan a lo largo de la doble hélice dejando las 2
cadenas separadas, listas para servir de molde en la síntesis de nuevas hebras
complementarias.
ADN polimerasa
Sintetiza la nueva cadena por ensamble de desoxirribonucleótidos. En eucariotas son
identificadas α, β, γ, δ y ε. Estas difieren entre sí, más comparten las siguientes
características:
Sustratos: desoxirribonucleótidos trifosfato. Proveen materia prima y energía
para la síntesis.
Necesitan cadena separada de ADN: funcionan sobre una hebra de ADN e
insertan los nucleótidos complementarios a los de la cadena patrón.
Incapaces de iniciar una nueva hebra: solo pueden elongar a una hebra
iniciadora o cebador.
Catalizan uniones diéster desde el hidroxilo del C3 de la desoxirribosa del
nucleótido terminal de la cadena iniciadora al fosfato del C5 del nucleótido que
ingresa.
Recorren las cadenas en sentido 3’5’
Replisoma
El conjunto de todas las proteínas comprometidas en la duplicación del ADN es un
complejo multienzimático que funciona como máquina de replicación.
Mecanismo de la replicación
Inicio de la replicación
1. Reconocimiento de la secuencia de iniciación: se realiza durante la fase G1, en la
hebra guía del ADN.
2. Formación del complejo multiproteico: en cada uno de los sitios donde debe
comenzar la síntesis. Primero se une la proteína iniciadora ORC, que agrega otras
proteínas que fijan la helicasa a la doble hebra. La helicasa es estimulada al ingresar
en la fase S por acción de 2 quinasas, una de ellas ciclina quinasa.
A medida que se separan las hebras se fijan proteínas A de replicación, que impiden que
las hebras se vuelvan a asociar para reformar la doble hélice. La activación del complejo
promueve la unión de proteínas, entre ellas la primasa y las polimerasas α, δ y ε. Todas
estas forman el Replisoma.
Cadena líder, conductora o adelantada (hebra sintetizada 5’
3’)
La ADN polimerasa recorre la cadena molde en el sentido 3’ 5’. Sobre esta la síntesis
prosigue sin interrupción.
1. Formación de cebador/ primer/ ARN iniciador: catalizada por una ARN polimerasa
denominada primasa, asociada a la ADN polimerasa α en eucariotas. Agrega
ribonucleósidos trifosfato en sentido 5’3’ para formar un segmento, de 10

MATÍAS ARIEL CABALLERO
nucleótidos, complementario del ADN molde. Inserta las bases complementarias,
excepto en adenina que inserta uracilo.
2. ADN polimerasa α: a continuación del cebador, agrega 20 desoxirribonucleótidos.
De inmediato una proteína llamada factor de replicación C (RFC) se une al extremo
3’ de este segmento ARN-ADN iniciador y desplaza a la polimerasa α y la primasa.
El principal papel de RFC es cargar la proteína antígeno nuclear de células
proliferantes (PCNA) sobre el ADN en formación.
3. PCNA-polimerasa δ: la PCNA rodea al ADN y promueve la puesta en funciones de
la polimerasa δ. Fija la polimerasa δ a la hebra guía y asegura la incorporación de los
nucleótidos necesarios para formar una cadena complementaria a la hebra original de
ADN, de manera ininterrumpida; el conjunto se desliza sobre la cadena molde en el
sentido de la síntesis. En la reacción de incorporación de cada nucleótido se libera
PPi, el cual es hidrolizado por pirofosfatasa en Pi.
n dATP + n dGTP + n dTTP + n dCTP -----> polímero 4n dRibonucleótidos + 4n PPi
La capacidad de la polimerasa para funcionar en forma continuada a lo largo de gran
número de nucleótidos es llamada procesividad. La polimerasa δ es altamente procesiva,
más que la α.
Cadena retardada o rezagada (hebra sintetizada 3’
5’)
La otra cadena no puede ser ensamblada de forma continua por la dirección contraria a la
del progreso de la ADN polimerasa; por esta razón, la síntesis se realiza en segmentos.
Pasa lo mismo que en la cadena adelantada, con la diferencia que la ADN polimerasa δ
completa un segmento de 200 nucleótidos (equivalente contenido en un nucleosoma), y
no toda la cadena, denominados fragmentos de Okazaki.
El proceso se repite varias veces, y el complejo polimerasa δ-PNCA debe desprenderse
al terminar cada fragmento de Okazaki y reinsertarse de nuevo para el próximo, después
que el complejo polimerasa α-primasa ha ensamblado el iniciador ARN-ADN del trozo
siguiente.
Se propuso que la hebra patrón de esta cadena rezagada debe formar un bucle para
presentarse al replicasoma en la dirección adecuada.
Corrección y reparación
Al tiempo que sintetiza la nueva hebra de ADN, la polimerasa δ detecta errores en el
apareamiento de bases. Su actividad exonucleasa 3’ 5’ le permite corregirlos.
Los trozos de ARN iniciador de cada fragmento de Okazaki son rápidamente eliminados
por ribonucleasas (ARNasa HI y nucleasa FEN1) que catalizan la hidrólisis de las uniones
fosfodiéster 3’-5’. Luego se sintetiza ADN para cubrir la brecha, por polimerasa δ o ε.
Separación
Se establecen enlaces fosfodiéster entre el hidroxilo del extremo 3’ y el fosfato 5’ de los
segmentos vecinos sintetizados en forma discontinua, acción a cargo de la ADN ligasa,
ocurre cuando el apareamiento entre las bases de la cadena neoformada y el molde es
correcto. 2 horquillas de replicación iniciadas en distintos puntos de la misma molécula
iniciadas en distintos puntos de la misma molécula se aproximan una a otra y terminan
MATÍAS ARIEL CABALLERO
por reunirse; las burbujas de replicación se confunden en una sola. Finalmente resultan 2
dobles hélices completas.
REPASO
Sitio de origen o iniciación
Secuencias específicas de bases que sirven de reconocimiento para el complejo de enzimas
y factores que inicia la replicación. Generalmente contiene secuencias ricas en pares A-T.
Complejo de reconocimiento
del origen (ORC)
6 subunidades. Agrega proteínas que fijan a la helicasa a la doble hebra al reconocer la
secuencia de iniciación.
Complejo de mantenimiento
del microcromosoma (MCM)
-------------------------------------------------
Replicones
“Burbujas” en la zona de replicación. Hay varios replicones, lo que aumenta la replicación,
más que si hubiese uno sólo.
Horquilla de replicación
Sitio en el cual las 2 cadenas se separan. Por cada burbuja se producen 2 horquillas de
replicación que avanzan en sentidos opuestos.
Helicasa
Cataliza la separación de las cadenas, con energía provista por hidrólisis de ATP. Su
acción comienza en la fase S, por acción de 2 quinasas, una de ellas ciclina quinasa.
Topoisomerasa I
Corta una de las hebras de la doble hélice y alivia la tensión por rotación libre de la cadena
seccionada sobre la otra. NO requiere energía.
Topoisomerasa II
Secciona las 2 hebras de ADN. Es dependiente de ATP.
Proteínas A de replicación
(RPA)
Estabilizan las monohebras e impiden su reasociación.
ADN polimerasa α
Síntesis de un trozo de ADN de 20 nucleótidos, continuación del cebador.
ADN polimerasa β
Participa en procesos de reparación de ADN.
ADN polimerasa γ
Interviene en la replicación del ADN mitocondrial.
ADN polimerasa δ
Síntesis de ADN a continuación del iniciador producido por polimerasa α-primasa.
ADN polimerasa ε
Síntesis y reparación de ADN. Tiene actividad exonucleasa 3’ 5’.
Replisoma
Conjunto de todas las proteínas comprometidas en la duplicación del ADN.
Cebador/primer/ARN
iniciador
Segmento de ARN de 10 ribonucleótidos complementario al ADN molde.
Primasa
Cataliza la síntesis del cebador. Agrega ribonucleósidos trifosfato en sentido 5’3’.
Inserta bases complementarias excepto en adenina que inserta uracilo. Está asociada a la
ADN polimerasa α.
Factor de replicación C
(RFC)
Se une al extremo 3’ del segmento ARN-ADN iniciador. Desplaza a la polimerasa α y la
primasa. Su principal función es cargar la proteína PCNA sobre el ADN en formación.
Antígeno nuclear de células
proliferantes (PCNA)
Rodea al ADN y promueve la puesta en funciones de la polimerasa δ. Fija la polimerasa y
asegura la incorporación de los nucleótidos.
Fragmentos de Okazaki
Segmento de 200 nucleótidos sintetizados por la ADN polimerasa δ en la cadena rezagada.
ARNasa HI y nucleasa
FEN1
Elimina los trozos de ARN iniciador, catalizan la hidrólisis de las uniones fosfodiéster 3’-
5’.
ADN ligasa
Une, mediante enlaces fosfodiéster 3’5’ los segmentos del ADN neoformado.
Reparación del ADN
En condiciones normales, la información genética almacenada en el ADN nuclear se
transite inalterada a través de las sucesivas divisiones celulares. Además de la eficiencia
de la replicación sobre un molde, esta perfección es debida a la existencia de sistemas de
corrección o reparación de errores cometidos durante la síntesis.
Mientras inserta nucleótidos complementarios sobre la hebra guía, la ADN polimerasa δ
realiza una tarea de detección de errores. Las polimerasas γ, δ y ε tienen actividad
exonucleasa 3’5’, que les permite eliminar la última base incorporada si no está
adecuadamente apareada.

MATÍAS ARIEL CABALLERO
A pesar de esta capacidad de autocorrección, el número de bases es muy grandes y
algunos errores son inevitables.
La reparación de errores o daños en el ADN comprende diferentes mecanismos:
Reparación de errores de apareamiento.
Reparación por escisión de base.
Reparación por escisión de nucleótidos.
Reparación por ruptura de las 2 cadenas.
Cada uno de estos procesos requiere la presencia de muchas proteínas reunidas en
diferentes complejos que cumplen las acciones de reparación:
Endo y exonucleasas: separación de la base o segmento de cadena mal apareado
o defectuoso.
Polimerasas: incorporación de bases correctas siguiendo el principio de
complementariedad con la cadena molde normal.
Ligasa: unión de trozo a reponer con los extremos cortados de la hebra de ADN
en reparación.
La ruptura de las cadenas puede ser causada por diversos agentes, principalmente por
especies reactivas de oxígeno y radiaciones ionizantes. Hay varios mecanismos para la
reparación del corte de ambas hebras de ADN.
Recombinación: intercambio de regiones equivalentes de la doble hélice de cromosomas
homólogos. Se utiliza la información existente en el cromosoma homólogo sano para
dirigir la reposición del sitio dañado en la otra doble hélice. Se requiere de un complejo
multiproteico.
Redistribución de genes en las gametas
Durante la meiosis se produce recombinación de ADN de cromosomas homólogos, con
intercambio de segmentos entre las 2 dobles hélices. Esto resulta en una redistribución de
los genes contenidos en los trozos intercambiados. Requiere energía provista por
hidrólisis de ATP y un conjunto de proteínas, entre ellas RAD51.
La recombinación contribuye a aumentar la variabilidad genética en organismos con
reproducción sexuada.
Telomerasas
Cuando se ha completado el proceso de duplicación, frente a los extremos 3’ de las hebras
molde queda un trozo de ARN iniciador. Estos segmentos son eliminados por ARNasa,
pero no pueden ser reemplazados por ADN, ya que las ADN polimerasas no funcionan
sin cebador, por lo que el cabo 3’ de cada cadena guía no puede ser duplicado.
Los cromosomas se hacen progresivamente más cortos en sucesivas divisiones celulares,
con pérdida irreparable de la información genética. Este problema es demorado por la
existencia de trozos que no contienen información, que se van acortando, existente en los
extremos de los cromosomas (telómeros).
El ADN telomérico descartable está formado por cientos de repeticiones de una secuencia
TTAGGG. En células con gran actividad mitótica, se insertan segmentos adicionales al
extremo 3’ del ADN telomérico preexistente, acción catalizada por telomerasas, que

MATÍAS ARIEL CABALLERO
contienen en su estructura un trozo de ARN utilizado como molde para ensamblar las
porciones con las cuales se elonga la cadena de ADN. Sobre la cadena neoformada, una
ADN polimerasa sintetiza la hebra complementaria para formar el ADN telomérico de
doble hélice.
Las telomerasas compensan el acortamiento producido por sucesivas divisiones. Las
células somáticas, que se dividen con escasa frecuencia, poseen una vida limitada por la
longitud de los telómeros de las células originales. Estos se acortan en cada replicación
hasta agotar la reserva de ADN telomérico (senescencia celular); la célula no puede seguir
reproduciéndose y muere. Las células cancerosas tienen gran actividad de telomerasas.
Antibióticos que bloquean la replicación
Novobiocina: inhibe la unión de ATP a las Topoisomerasas.
Ciprofloxacina: bloquea la última etapa de la reacción de las Topoisomerasas y el cierre
de la ruptura de la hebra de ADN.
----------------------------------------------------------------------------------------------------------
TRANSCRIPCIÓN: ADN a ARN
La síntesis de ARN y ADN presentan similitudes:
Una polimerasa cataliza el ensamble de nucleótidos para formar una hebra
complementaria de otra de ADN que sirve de guía o molde.
Los 2 procesos utilizan nucleósidos trifosforados, con diferencias lógicas
exigidas por la distinta composición en nucleótidos de ARN.
La cadena formada copia la información contenida en el trozo de ADN utilizado como
plantilla. Por este motivo se llama transcripción. Cada gen se transcribe en toda su
extensión, incluyendo las porciones codificantes (exones) y las no codificantes (intrones).
Como se sintetiza ARN sobre una de las cadenas de ADN, se dice que la transcripción es
asimétrica. La hebra molde de ADN sobre la que se realiza la transcripción es llamada
antisentido o no codificante; la cadena no transcripta tiene la misma secuencia que el
ARN (admitiendo cambio de T por U), es la hebra con sentido o codificante.
La unión de los nucleótidos es catalizada por ARN polimerasas dependientes de ADN.
Todos los ARN se generan en el núcleo; una vez completada la síntesis, las moléculas de
ARN se dirigen al sitio de donde cumplirán su función.
Transcripción en procariotas
La ARN polimerasa es un complejo oligomérico integrado por subunidades diferentes.
Una contiene el sitio catalítico responsable de la formación de enlaces fosfodiéster 5’3’,
mientras otra se encarga de fijar la holoenzima a la cadena de ADN molde. La subunidad
σ reconoce los segmentos del ADN donde iniciar la transcripción (promotores).
Si el sitio se encuentra hacia el extremo 5’ se dice que está corriente arriba (-); si es hacia
el extremo 3’ es corriente abajo (+).
El promotor presenta 2 módulos ubicados 10 y 35 bases hacia el extremo 5’ del segmento
a transcribir. En estos sitios se encuentran secuencias específicas denominadas cajas. El
MATÍAS ARIEL CABALLERO
módulo en posición 10 tiene una secuencia TATAAT, llamada caja de Pribnow. El de
posición 35 tiene secuencia TTGACA.
Desenrollamiento ADN: La ARN polimerasa actúa al principio como desenrollasa y
también reestablece la doble hélice después de la transcripción.
Transcripción: la enzima toma como patrón solo una hebra. En presencia de todos los
ribonucleósidos trifosforados, la enzima comienza con la polimerización insertando un
nucleótido con base púrica como primera unidad de la cadena. Este nucleótido conserva
sus 3 fosfatos, sirviendo como señal de extremo inicial. La unión de cada nucleótido libera
pirofosfato, que es desdoblado por pirofosfatasa.
n ATP + n CTP + n GTP + n UTP ARN + 4n PPi
la polimerización progresa en la dirección 5’ 3’ de la hebra neoformada, en sentido
antiparalelo al de la cadena guía.
Final de síntesis: cuando se unieron 10 nucleótidos, la subunidad σ se desprende. El final
de la síntesis es indicado por una secuencia específica en el ADN, que actúa como señal
de terminación. Poco antes del sitio final de la transcripción existen sectores ricos en CG
repetidas; la cadena sintetizada tiene en este segmento trozos autocomplementarios y
puede volver sobre sí misma para formar una horquilla, la cual retrasa o detiene el avance
de la ARN polimerasa. También hay proteínas que libera la cadena de ARN sintetizada.
Transcripción en eucariotas
Las células poseen en el núcleo al menos 3 polimerasas (I, II y III), enzimas que se
desplazan en sentido 5’3’, dirección 3’5’ sobre el molde formado, cada una
encargada de la síntesis de diferentes clases de ARN,:
ARN polimerasa I: en el nucléolo. Cataliza síntesis de ARNr.
ARN polimerasa II: en nucleoplasma. Cataliza síntesis de ARNm y otros tipos
(pequeños y largos, no codificantes).
ARN polimerasa III: en núcleo. Cataliza síntesis ARNt, ARNr 5S, ARNpc y ARNpn.
Existe una cuarte en mitocondrias. Todas las enzimas están formadas por 12 o más
subunidades. (mnemotecnia: RE-MA-TE // I-II-III). Las ARN polimerasas no tienen
capacidad para corregir errores producidos en el apareamiento de bases.
Las 3 enzimas pueden diferenciarse por su sensibilidad a la α amanitina: la I es insensible,
la II es inhibida por muy bajas concentraciones, la III por altas.
Factores de transcripción
Requieren de proteínas llamadas factores basales o generales de transcripción, que se
unen al ADN y a la polimerasa, la ubican en la posición correcta en el promotor, colaboran
en la separación de la doble hélice y promueven la iniciación de la transcripción. Cumplen
un papel semejante al de la subunidad σ de procariotas, pero no forman parte de la ARN
polimerasa. Son designadas con iniciales TF seguidas del número de la polimerasa.
Hay un factor común presente en el complejo de iniciación de las 3 polimerasas; es la
proteína de unión a la TATA box (TBP)

MATÍAS ARIEL CABALLERO
Transcripción y empaquetamiento del ADN
El superenrollamiento en los nucleosomas puede entorpecer la iniciación de la
transcripción cuando el sitio promotor queda cubierto. En este caso las histonas son
desplazadas de su posición para dejar libres las zonas promotoras y permitir el acceso del
complejo de transcripción.
La metilación de bases del ADN y la acetilación de las histonas influyen sobre la
estructura de cromatina y actividad de los cromosomas. El ADN altamente metilado se
encuentra en mayor proporción en los genes inactivos; en cambio cuando las histonas se
acetilan, la cromatina se relaja, lo que favorece la transcripción.
ARN MENSAJERO (ARNm)
Síntesis de ARN precursor del mensajero
Síntesis catalizada por la ARN polimerasa II. Se sintetiza una molécula de ARN
precursor, más largo que el ARNm.
Promotor
Comprende 3 módulos:
TATA box: en posición 25, secuencia consenso heptanucleotídica formada por
restos timina y adenina. En su mayoría están flanqueadas por secuencias ricas en
GC.
CAAT y GC box: en posiciones 45 y 110 respectivamente. Son llamadas
elementos genéticos de acción cis. A estos sitios se unen factores de transcripción
esenciales para que la síntesis comience en el lugar correcto.
Activadores y represores
Proteínas que se unen a secuencias específicas del ADN situadas a miles de pares de bases
del promotor. Pueden estar corriente arriba, abajo o dentro del trozo de ADN transcripto.
Las zonas de ADN sobre las cuales se ejercen acciones activadoras son llamadas
potenciadoras o aumentadoras.
Otros factores de transcripción
Proteínas que se unen con gran afinidad a secuencias específicas en promotores, a
regiones regulatorias corriente arriba y a potenciadores. El control de la maquinaria
transcripcional de la ARN polimerasa II es mediado por una red de factores de
transcripción, muchos activados por hormonas. Los sectores a los que se unen se
denominan elementos de respuesta.
Formación del complejo
TFIID o factor de transcripción IID: se une a la caja TATA. Está compuesto por la
TBP y polipéptidos llamados factores asociados a TBP (TAF).
Complejo de iniciación de la transcripción: a continuación, se agregan otros
factores (TFIIA, TFIIB, TFIIF, TFIIE, TFIIH) y la polimerasa II. TFIIH tiene
actividad helicasa y quinasa; esta última cataliza la fosforilación de la polimerasa II.
MATÍAS ARIEL CABALLERO
La polimerasa II fosforilada se desprende del complejo y comienza la transcripción
desplazándose sobre la hebra guía de ADN. Los factores de transcripción se disocian, se
separan del promotor y quedan disponibles para comenzar con otra polimerasa II.
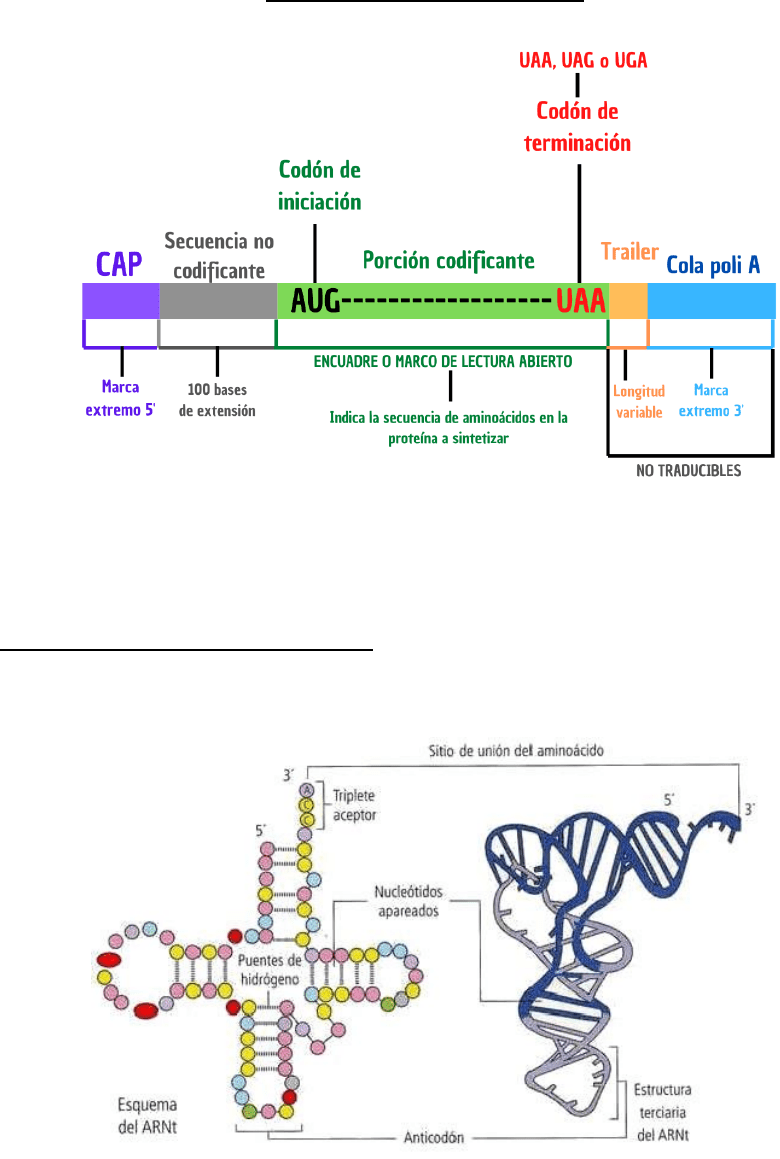
Formación del CAP
¿Qué es?: cadena de ARN en formación modificado por unión de una molécula
de GTP mediante enlace 5’-5’, cuyo nitrógeno 7 es metilado, formando en el
terminal 5’ de la cadena 7-metilguanosina trifosfato.
¿Para qué sirve?: reconocimiento del extremo 5’ del ARNm por el complejo de
iniciación de la traducción, y protección ante fosfatasas y exonucleasas.
Cola de poli A
¿Qué es?: cadena de un trozo de 100 a 200 nucleótidos de adenina en el extremo
3’ de la cadena. Sólo muy pocos no se poliadenilan, por ejemplo, para histonas.
¿Para qué sirve?: contribuye a la eficiencia de la traducción y da estabilidad al
ARN.
¿Cómo se forma?: una endonucleasa específica secciona la cadena de ARN y
una poli A polimerasa sintetiza un segmento adicional de 100 a 200 nucleótidos
de adenina, con ATP como donante de las unidades.
Los ARN sintetizados por la polimerasa II son liberados en el nucleoplasma donde forma
parte del ARN nuclear heterogéneo (ARNnh) que incluye también a ARNm maduros.
Mediador
Complejo formado por múltiples subunidades cuya
función es la regulación de la iniciación y elongación de
la transcripción, de la expresión de transcriptos de la
polimerasa II, es decir, la mayoría de los genes que
codifican proteínas y ARN no codificantes, y del
procesamiento del ARNm.
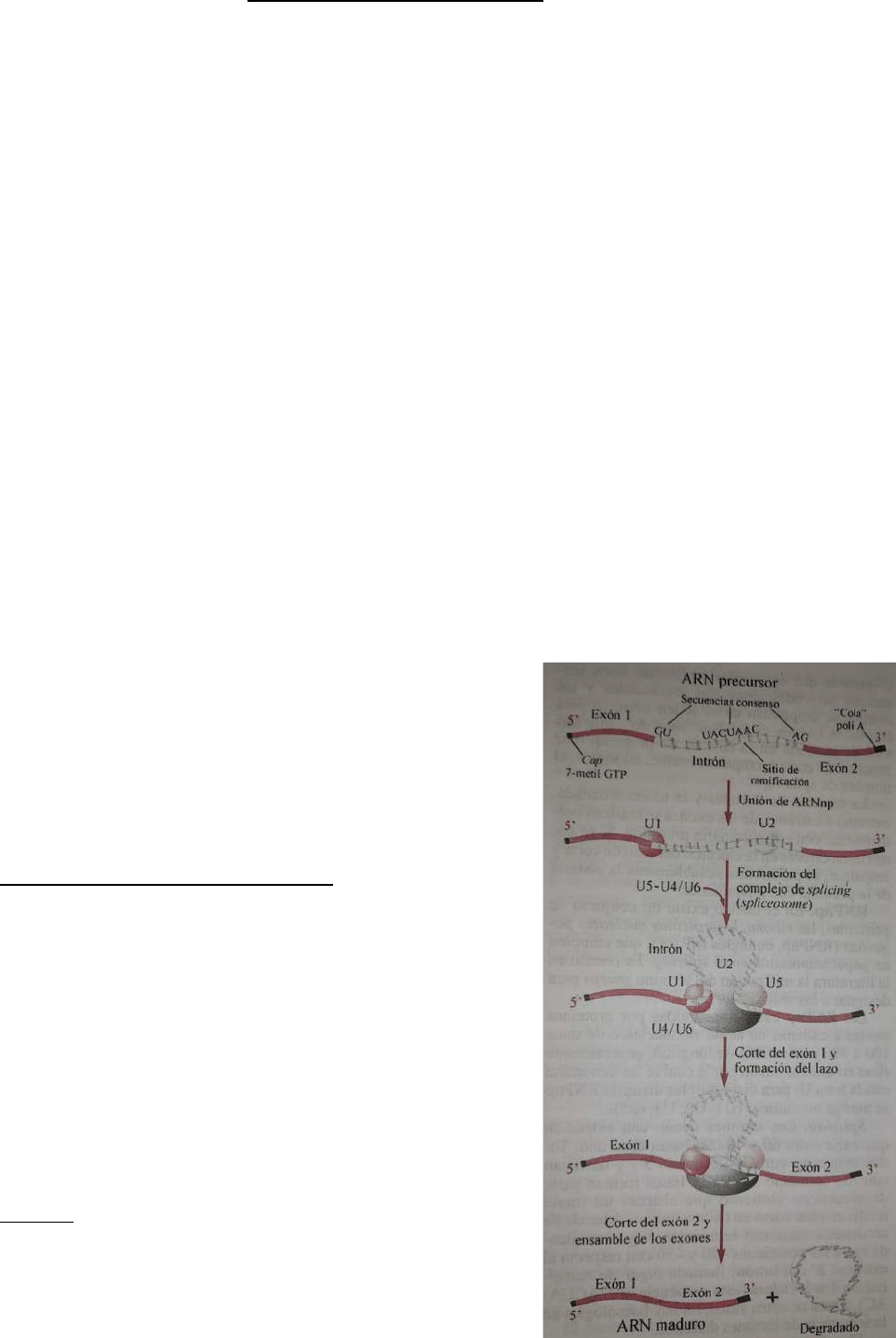
Procesamiento del ARNm precursor
La gran mayoría de las cadenas de ARNm primario
contiene intrones que son necesarios eliminar; estos
segmentos no codificantes son seccionados y los exones
se empalman en el orden correcto para formar la cadena
de ARNm maduro, que servirá para la síntesis de
proteínas.
Ribonucleoproteínas nucleares pequeñas (RNPnp):
están formadas por proteínas unidas a cadenas de ARN
ricas en uracilo, por lo que suelen llamarse U y un
número.
Splicing
Todos los intrones empiezan con GU (extremo 5’) y
terminan con AG (extremo 3’). Estas bases forman parte
de secuencias consenso que abarcan un tramo corto en

MATÍAS ARIEL CABALLERO
cada extremo; además de secuencias terminales, hay una entre las bases 20 y 50 llamada
lugar de ramificación.
El splicing se inicia con la formación de un complejo integrado por varias RNPnp y
proteínas unidas al ARN precursor; el conjunto se llama spliceosome.
U1 (RNPnp) posee un tramo de ARN con secuencia complementaria a la existente en el
extremo 5’, esto le permite aparearse al ARN precursor. Por un mecanismo similar la
RNPnp U2 se une a la secuencia de ramificación. Luego se agregan U4 y U6, en un solo
bloque, y U5.
El ARN precursor es seccionado en el extremo 5’ por medio de transesterificación, es
decir, se establece una nueva unión fosfodiéster entre el extremo 5’ del intrón y el OH del
C2 de la ribosa de un nucleótido de adenina en el sitio de ramificación. Como resultado
se forma un lazo.
A continuación, se escinde la unión del extremo 3’ y éste queda libre. Una nueva
transesterificación forma un puente diéster 3’-5’ entre el extremo 3’ del exón con el 5’
del otro; el intrón en forma de lazo es liberado y degradado por hidrólisis en el núcleo.
Procesamiento diferencial
Poliadenilación: El proceso de maduración del ARN mensajero permite generar
proteínas diferentes a partir del mismo gen. En el transcripto primario existe a veces más
de un sitio donde insertar la cola de poli A; según el lugar en el que se efectué el corte y
la poliadenilación, resultarán diferentes tipos de ARNm maduros, que codifican proteínas
diferentes.
Splicing alternativo: también es posible empalmar todos los exones presentes en el
transcripto primario, o sólo algunos de ellos (splicing alternativo). El splicing alternativo
resulta un mecanismo que determina qué información es transmitida finalmente entre
transcripción y traducción.
Edición del ARNm: se introducen o eliminan bases, así se modifica el significado de un
codón, crear un sitio de splicing o alterar la estructura de ARN.
Los genes de los cuales se origina más de un ARNm maduro son denominados unidades
de transcripción compleja.
Enfermedades por alteraciones del splicing: principalmente son síndromes con
compromiso de los sistemas muscular o nervioso. Distrofia miotónica, atrofia muscular
espinal, ataxia telangiestástica; en otros hay predisposición a enfermedades autoinmunes,
envejecimiento prematuro o transformación maligna de células. Las talasemias también
pueden ser producidas por alteraciones.
ARNm maduro
Una vez completadas las modificaciones postranscripcionales, el producto terminal es el
ARN maduro o ARNm, exportado al citoplasma a través de los poros de la membrana
nuclear. Está formado por:
MATÍAS ARIEL CABALLERO
Transcriptoma: conjunto de ARN contenido en una célula. Aunque todas las células de
un organismo tienen el mismo ADN, el transcriptoma varía de un tipo celular a otro y en
distintos momentos en una misma célula, influido por factores como hormonas y otros
agentes.
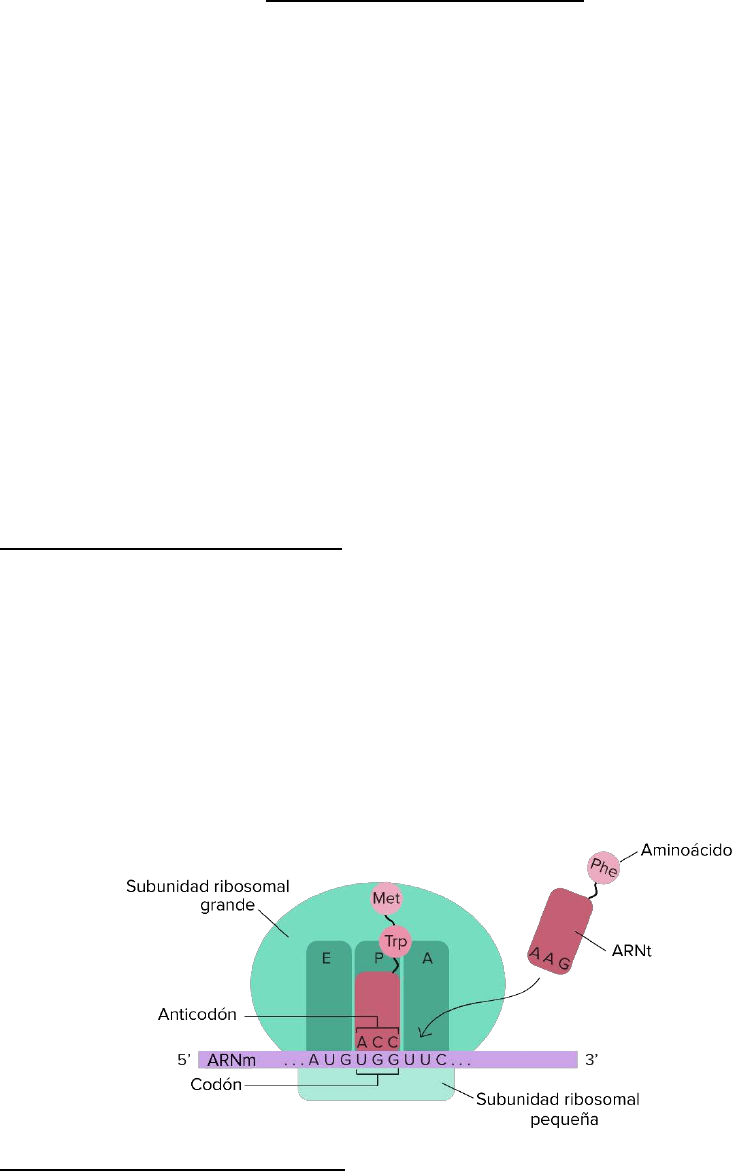
ARN DE TRANSFERENCIA (ARNt)
Este tipo de ARN es encargado de unirse a aminoácidos libres en el citosol y
transportarlos hacia el lugar de su ensamble en cadenas de nuevas proteínas.
Su extremo 3´se une al aminoácido y es idéntico para todos los ARNt (secuencia CCA).
La especificidad radica en el asa central, donde se encuentra un triplete anticodón,
complementario del codón correspondiente al aminoácido transportado por el ARNt.
El ARNt actúa como una molécula intermediaria o adaptadora que reconoce una
secuencia determinada de nucleótidos en el ARNm (codón) y permite ubicar en su sitio
al aminoácido correspondiente.
Debido a la redundancia del código puede existir más de un ARNt para algunos
aminoácidos.

MATÍAS ARIEL CABALLERO
El enfrentamiento de la 3ra base del codón con la primera del anticodón suele ser menos
estricto que el de las otras 2, lo que explica la posibilidad de apareamiento de un ARNt
con más de un triplete.
Síntesis de ARNt
Catalizada por ARN polimerasa III en el núcleo. El precursor debe ser procesado para
eliminar un intrón y modificar bases.
Promotor
Tiene 2 promotores (cajas A y B), situados corriente abajo del sitio de iniciación, dentro
de la zona correspondiente a los propios genes.
Formación del complejo
TFIIC: se une a las secuencias promotoras A y B. Actúa como factor de ensamble que
permite ubicar al TFIIB, 50 pares de bases corriente arriba de la caja A. TFIIB contiene
la subunidad de TBP, favorece la unión y posicionamiento de la polimerasa III para iniciar
la transcripción.
Procesamiento de ARNt precursor
Se sintetiza un ARN precursor que debe ser procesado en el núcleo antes de pasar al
citoplasma. Las modificaciones comprenden:
Metilación.
Remoción de segmentos de la cadena.
Unión de fragmentos para formar la molécula final.
Adición de la secuencia CCA en el extremo 3’ terminal: el agregado se efectúa
de una por vez, catalizado por nucleotidil transferasa.
El extremo 5’ de los ARNt se genera por acción de ribonucleasa P (ribozima).
ARN RIBOSOMAL (ARNr)
Asociado a proteínas, este tipo de ARN integra los ribosomas, partículas vinculadas a la
síntesis de proteínas. A fin de atender la gran demanda de moléculas de ARNr en la célula,
existen múltiples repeticiones de los genes que codifican para ARNr.
Síntesis de ARNr
Los ribosomas están formados por 2 partículas: la mayor de 60S formada por 3 moléculas
de ARN (5S, 5,8S y 28S) y 45 proteínas diferentes; la menor de 40S compuesta por una
molécula de ARN 18S y 30 proteínas.
La síntesis de ARN mayores (28S, 18S y 5.8S) es catalizada por ARN polimerasa I en el
nucléolo, donde se forma un trozo precursor de 45S. estos son liberados por ruptura del
ARNr primario. A veces se encuentran intrones, por lo que requiere un proceso semejante
al descripto para ARNm.
El ARNr 5S es ensamblado fuera del nucléolo por ARN polimerasa III.
Promotores
Los promotores se extienden unos 50 pares de bases que comienzan en la posición 100.
A este sitio se lo llama elemento de control corriente arriba (UCE).
MATÍAS ARIEL CABALLERO
Formación del complejo
2 factores se unen a las secuencias promotoras: factor de unión corriente arriba (UBF)
y factor 1 de selectividad (SL1), que contiene la subunidad TBP. A estos factores se
fijan la polimerasa I y otras proteínas que forman el complejo de iniciación.
Transcripción de ARNr de 5S
Los genes son transcriptos por la polimerasa III. Los promotores tienen una región de
control (caja C) ubicada corriente abajo del sitio de comienzo de transcripción, y otra
(caja A) de +50 a +65. Después que el factor TFIIIA se una a la caja C se forma un
complejo TFIIIC y TFIIIB (contiene TBP). La polimerasa III se fija al complejo y se
inicia la transcripción.
Una vez liberadas las moléculas de ARNr se asocian con las proteínas correspondientes.
La porción de 18S, unida a proteínas, forma la partícula ribosomal pequeña. El ARN 5S
se une a los ARN de 28S y 5.8S y a un conjunto de proteínas para formar la partícula
mayor.
Procesamiento de ARNr precursor
Por acción de la ARN polimerasa I se sintetiza una larga cadena de 45 S que comprende
las 3 moléculas mayores de ARN (28S, 18S y 5.8S). este material sufre cortes para
generar los ARNr maduros. El procesamiento comprende también metilaciones en el
hidroxilo del C2 de las ribosas. En estas metilaciones intervienen partículas de ARNpn.
ARNr maduro
Se une a proteínas para constituir las subunidades de los ribosomas. Cuando las 2
porciones se unen para formar la partícula ribosomal completa, queda una hendidura por
la cual se desliza el ARNm durante la traducción.
Enzimas ribonucleicas o ribozimas
En diversos organismos existen ácidos ribonucleicos que se comportan como enzimas,
con todas las propiedades de catalizadores biológicos, se los llama ribozimas.
Las ribozimas pueden ser:
Hidrolíticas: capacidad para escindir enlaces fosfodiéster entre nucleótidos en
cadenas de ARN. Algunas son autocatalíticas; otras actúan como endonucleasas
en el procesamiento de precursores de ARNt.

MATÍAS ARIEL CABALLERO
Splicing: en la mayoría de los casos, las ribozimas catalizan el corte de intrones y
empalme de los exones adyacentes. El propio intrón está comprometido en la
acción enzimática.
Formación de uniones peptídicas: la formación de uniones peptídicas en la
síntesis de cadenas de proteínas es catalizada por peptidil transferasa, una
ribozima localizada en la partícula mayor de los ribosomas.
El ARN puede contener información codificada en la secuencia de sus bases y duplicarse
por mecanismos similares a los del ADN. El ARN forma estructuras secundarias y se
pliega en diversas conformaciones.
El ARN se comporta muy bien como intermediario en los procesos de lectura y traducción
de la información genética.
ADN polimerasa transcriptasa inversa
Transcripción inversa: proceso que sintetiza ADN sobre un molde de ARN.
En virus de ARN se descubrió una enzima, designada transcriptasa inversa, que cumple
funciones de ADN polimerasa dependiente de ARN. Se la encuentra en virus agentes de
tumores y otras patologías, llamados retrovirus.
Cuando un retrovirus infecta una célula, la enzima cataliza, en sentido 5’3’, el ensamble
de una cadena de ADN complementaria de la hebra de ARN invasor. La actividad
ribonucleasa de la misma enzima promueve la hidrólisis de la cadena original de ARN
molde y libera la hebra de ADN neoformada. Este sirve de guía para armar otra cadena
de ADN complementario y obtener una doble hélice con la información genética del ARN
viral.
Esta doble hélice llamada ADN proviral, posee secuencias idénticas en ambos extremos,
denominados terminales largos repetidos; estos contienen señales para su integración en
el ADN de la célula hospedadora y posterior transcripción a un ARN idéntico al viral.
Las telomerasas también tienen actividad transcriptasa inversa.
Antibióticos que bloquean la transcripción
Actinomicina D: se fija a la doble hélice del ADN, impidiéndole actuar como molde para
la síntesis de ARN.
Rifamicina-rifampicina: actúan sobre la ARN polimerasa e impiden la formación del
primer enlace fosfodiéster 5’ 3’ del ARN.
----------------------------------------------------------------------------------------------------------
BIOSÍNTESIS DE PROTEÍNAS
CÓDIGO GENÉTICO
La secuencia de bases púricas y pirimídicas de las hebras de ARN mensajero transcriptas
de genes que codifican proteínas provee las directivas para el ordenamiento de los
aminoácidos.
Un aminoácido es especificado por un conjunto de 3 bases consecutivas o terno. Se ha
impuesto el uso de la palabra triplete para designar un grupo de 3 bases. Con las 4 bases
se pueden componer 64 tripletes diferentes.
Este documento contiene más páginas...
Descargar Completo
Replicación ADN, Transcripción y Traducción.pdf
 Estamos procesando este archivo...
Estamos procesando este archivo...
 Lamentablemente la previsualización de este archivo no está disponible. De todas maneras puedes descargarlo y ver si te es útil.
Lamentablemente la previsualización de este archivo no está disponible. De todas maneras puedes descargarlo y ver si te es útil.
Descargar
 Estamos procesando este archivo...
Estamos procesando este archivo...
 Lamentablemente la previsualización de este archivo no está disponible. De todas maneras puedes descargarlo y ver si te es útil.
Lamentablemente la previsualización de este archivo no está disponible. De todas maneras puedes descargarlo y ver si te es útil.