Elisa Lara. Medicina, UNCO.
2. ESTRUCTURA Y CONFORMACIÓN DEL ADN.
I. ESTRUCTURA DEL ADN.
Polímero compuesto por cuatro nucléotidos: Adenina, guanina, citosina y timina, más azúcares fosforilados.
Doble hélice con esqueleto azúcar-fostato en el exterior de la molécula. Las bases están en el interior,
orientadas de tal forma que se producen enlaces puente hidrógeno entre purinas y pirimidinas de cadenas
opuestas.
El apareamiento de bases es muy específico: T-A (doble enlace) y G-C (triple enlace).
Según la ley de Chargaff: - Cantidad de adenina es siempre equivalente a la de timina.
- Cantidad de citosina es siempre equivalente a la guanina.
A causa de esta especificidad en el apareamiento de bases, las dos hebras son
complementarias: Cada hebra
contiene toda la información necesaria para especificar la secuencia de bases de la otra.
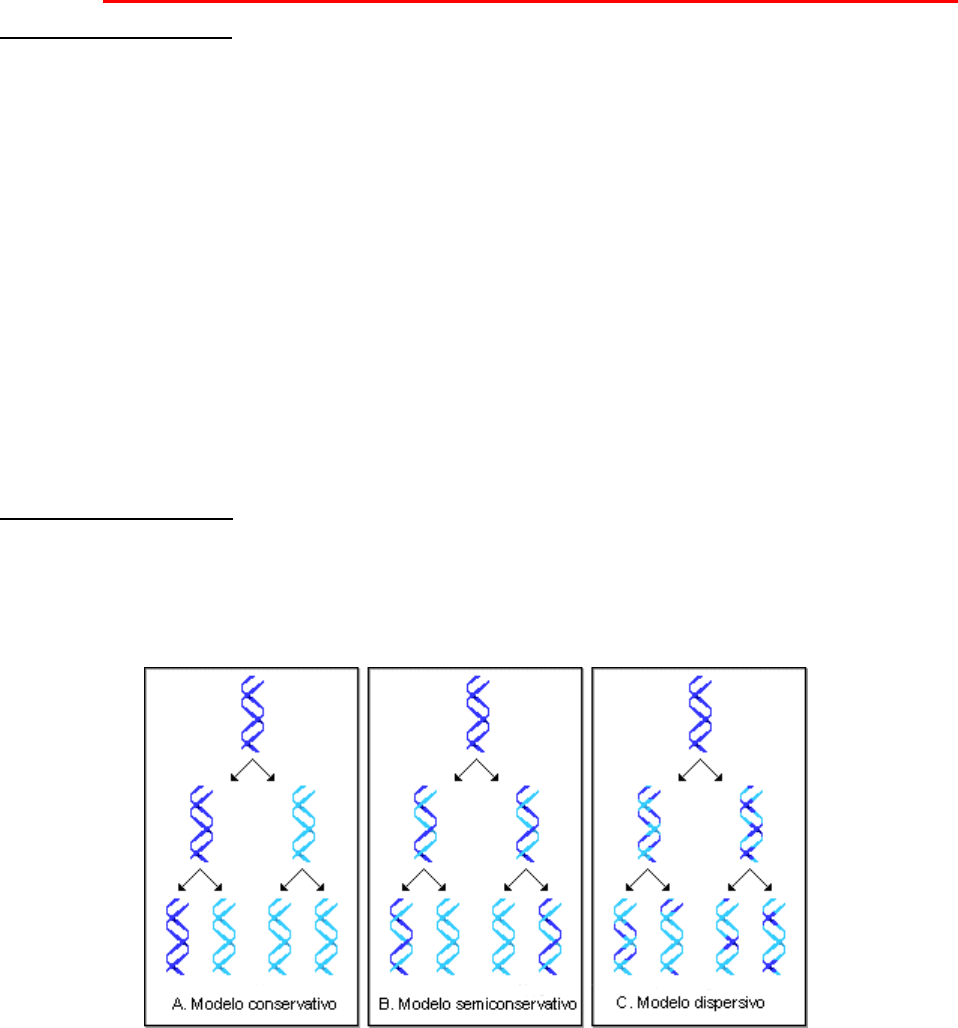
II. REPLICACIÓN DEL ADN.
Las dos hebras de la molécula de ADN se pueden separar y sirvenc como moldes para la síntesis de nuevas
hebras complementarias, cuya secuencia sería dictada por la especificidad del apareamiento de bases. Esto se
denomina: Replicación semiconservativa, porque una hebra de ADN progenitora se conserva en cada una de
las dos moléculas hijas de ADN.
ADN POLIMERASAS:
Las células contienen diferentes tipos de ADNpol, con funciones distintas en la replicación y reparación del ADN.
Las células eucariontes contienen 3 tipos de
ADNpol: α, δ, ε, que funcionan en la replicación nuclear. Otra
ADNpol diferente, la γ, se localiza en las mitocondrias y es reponsable de la replicación mitocondrial.
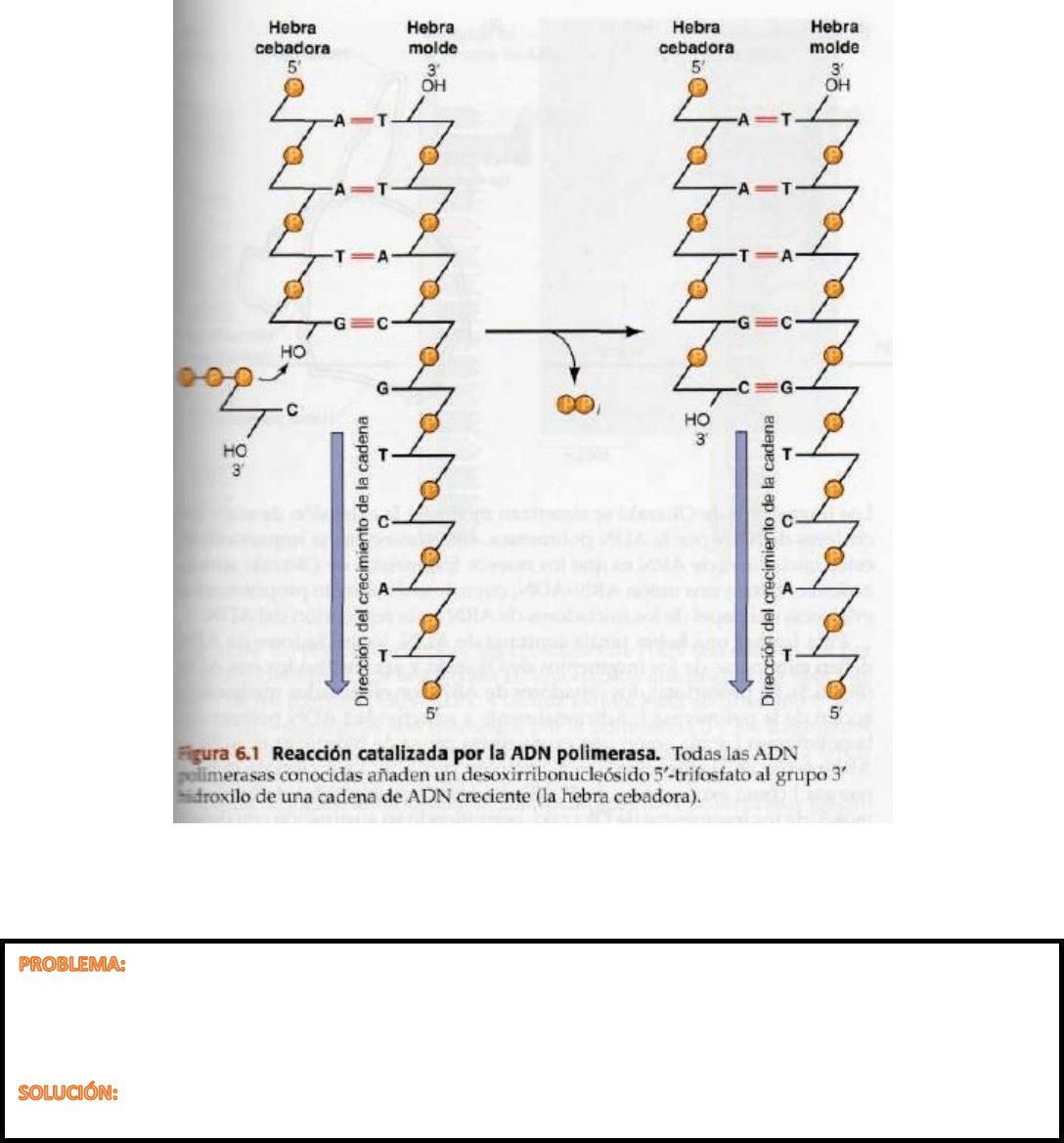
Todas las ADNpol comparten dos características fundamentales:
- Sintetizan ADN solo en dirección 5’→3’. Añadiendo un dNTP al grupo 3’ hidroxilo de una cadena creciente.
-
Pueden añadir un nuevo dNTP solo a una hebra cebadora ya existente que se encuentra unida mediante
puentes de hidrógeno a una hebra molde; no son capaces de iniciar la síntesis de ADN de novo, mediante la
catalización de dNTP's libres.
Elisa Lara. Medicina, UNCO.
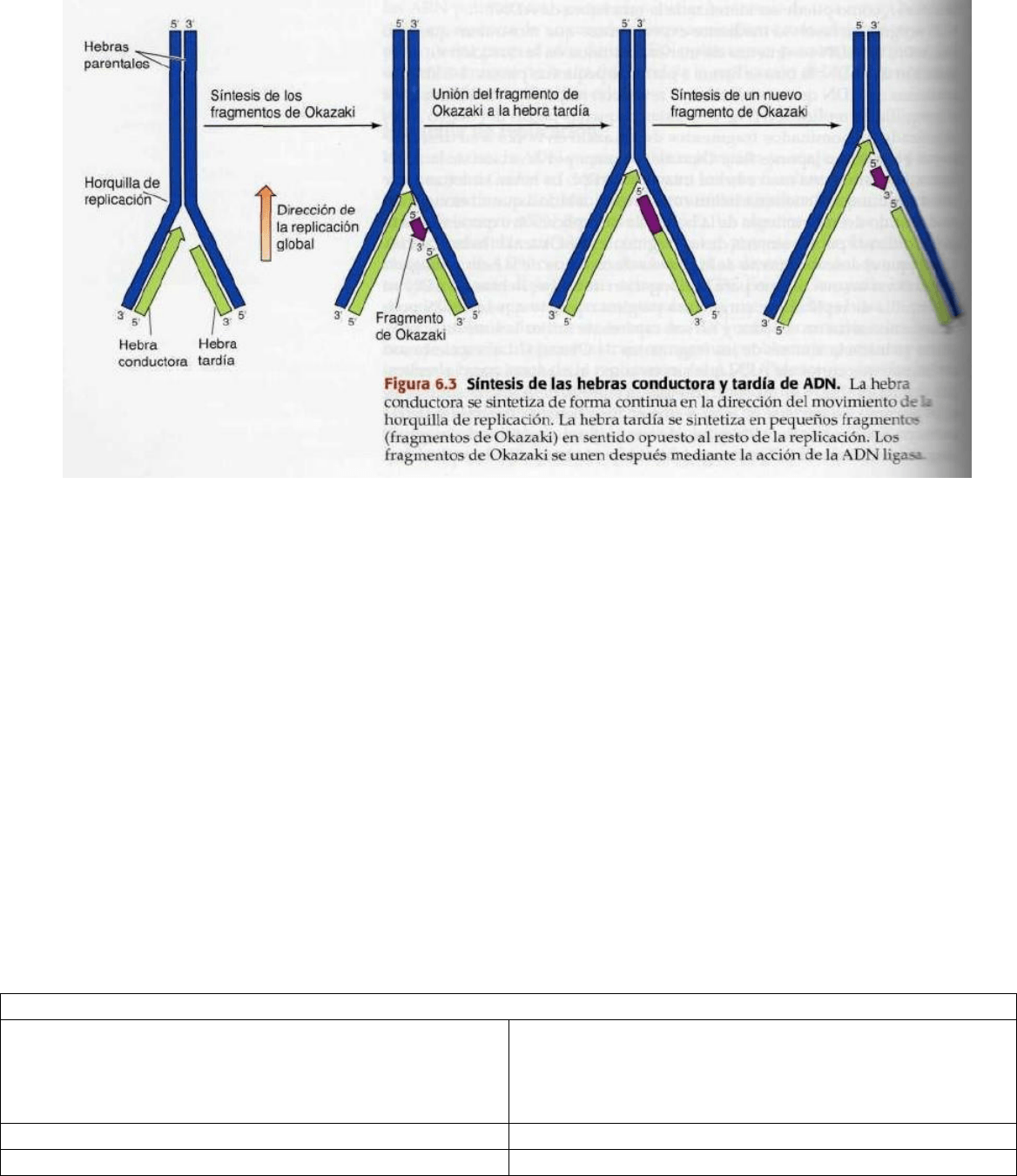
HORQUILLA DE REPLICACIÓN:
Solo una hebra de ADN se sintetiza de manera continua, en dirección 5’→3’, la otra se forma a partir de pequeñas
piezas discontinuas de ADN que se sintetizan al revés con respecto al movimiento de la horquilla de replicación.
Estas pequeñas piezas de ADN sint. se denominan
Fragmentos de Okazaki.
Puesto que las dos hebras de la doble hélice de ADN se disponen en direcciones opuestas (antiparalelas),
la síntesis continua de dos hebras en la horquilla de replicación requeriría que una de las hebras se sintetizara en
sentido 5’→3’, mientras que la otra se debería sintetizar en sentido opuesto: 3’→5’. Pero la ADNpol solo tiene la
posibilidad de catalizar la polimerización de los dNTP's en sentido 5’→3’.
Fragmentos de Okazaki.
Elisa Lara. Medicina, UNCO.
Los fragmentos de Okazaki se unen mediante la acción de la
LIGASA, formando una nueva hebra intacta de ADN.
La hebra sintetizada de forma continua se llama:
“hebra conductora”, debido a que su elongación, en el sentido
del movimiento de la horquilla de replicación, expone el molde que se utilizará para la síntesis de los fragmentos
de Okazaki, es decir, la
“hebra tardía”.
El incio de la síntesis de los fragmenos de Okazaki se debe gracias a fragmentos cortos de ARN, que sirven como
iniciadores para la replicación del ADN. Al contrario que la síntesis de ADN, la síntesis de ARN es capaz de iniciarse
de novo, y una enzima llamada PRIMASA, sintetiza los fragmentos cortos de ARN llamados PRIMERS. Estos
primers son complementarios a la hebra rezagada molde en la horquilla de replicación.
Los fragmentos de Okazaki se sintetizan mediante la extensión de estos primers mediante la ADNpol. Una
consecuencia importante de estos primers es que los nuevos fragmentos de Okazaki sintetizados contienen una
unión ADN-ARN, lo que demuestra el papel iniciador del ARN en el proceso de replicación.
Para formar una hebra tardía continua de ADN los primers deben eliminarse de los fragmentos de Okazaki y ser
sustituidos mediante la acción ARNasa H (enzima que degrada la hebra de ARN del híbrido ADN-ARN y que tiene
actividad exonucleasa). Los huecos resultantes son rellenados por la POLIMERASA δ, y los fragmentos de ADN
son unidos mediante la
LIGASA, generando una hebra tardía de ADN intacta.
ACCIONES ADN POLIMERASAS EN EUCARIONTES.
ADNpol α
Forma un complejo con la primasa, y funcionan
sintetizando fragmentos cortos de ADN-ARN, durante la
síntesis de la hebra tardía y en los orígenes de
replicación.
ADNpol δ
Función polimerasa en la hebra conductora.
ADNpol ε
Función polimerasa en la hebra tardía.
Elisa Lara. Medicina, UNCO.
PROCESO DE REPLICACIÓN:
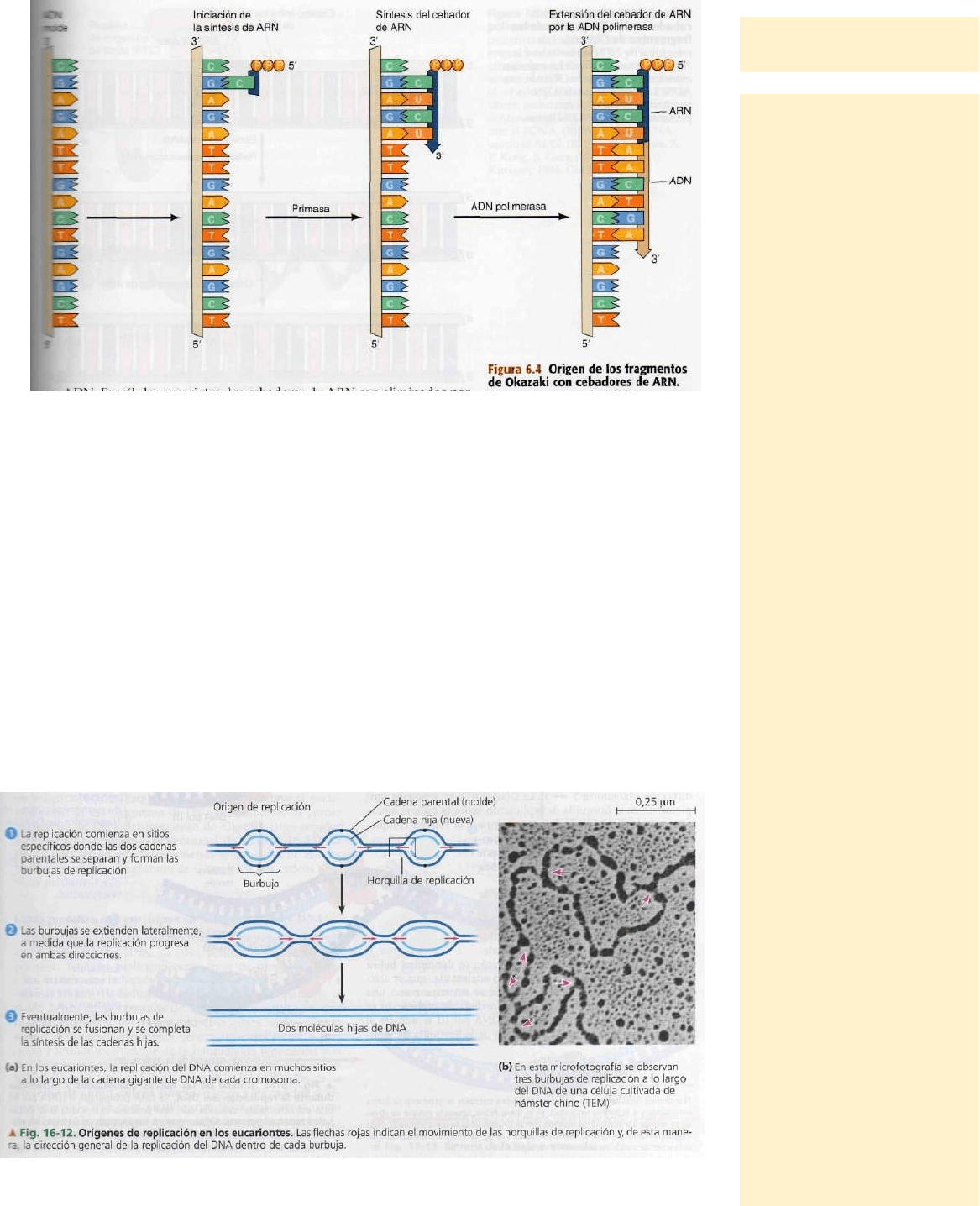
1.- Orígenes de replicación:
La replicación de una molécula de ADN comienza en sitios especiales llamados:
“orígenes de replicación”. Los cuales son tramos del ADN con una secuencia de
nucleótidos específica. Las proteínas que inician la replicación del ADN reconocen estas
secuencias y se fijan al ADN, separando las dos cadenas y abriendo una burbuja de
replicación.
La replicación del ADN progresa entonces en ambas direcciones. Un cromosoma
eucarionte contiene cientos o miles de orígenes de replicación. Se forman burbujas de
replicación múltiples que eventualmente se fusionan, acelerando de este modo, la
copia de las moléculas de ADN muy largas.
En cada extremo de una burbuja de replicación hay una
horquilla de replicación.
No hay que olvidar que las
ADNpol no son las únicas
proteínas que permiten el
proceso de replicación.
- Proteínas que
aumentan actividad
ADNpol.
- Proteínas de
enganche
deslizante: Que
sitúan a la
polimerasa en el
cebador y
mantienen su
asociación estable
con el molde.
- Proteínas de
enganche de carga:
Fijan las proteínas
de enganche
deslizante al ADN.
El anillo formado por el
enganche deslizante
mantiene la asociación
de la polimerasa con el
molde conforme avanza
la replicación, lo que
hace posible la síntesis
ininterrumpida de miles
de nucleótidos de ADN.
- Proteínas de unión
a cadena simple:
Estabilizan la
cadena molde de
ADN desenrrollada,
manteniéndola en
un estado de hebra
única extendida.
PROTEÍNAS ACCESORIAS.

Elisa Lara. Medicina, UNCO.
2.- Elongación de una cadena nueva de ADN.
La elongación de una cadena nueva de ADN en la horquilla de replicación se cataliza por las enzimas
ADNpol δ y ε. A
medida que los nucleótidos individuales se alinean con los nucleótidos complementarios a lo largo de la cadena molde
de ADN, la ADNpol los añade, uno a uno al extremo en crecimiento de la nueva cadena de ADN. La velocidad de
elongación es alrededor de 50 nucleótidos por segundo en células humanas.
Cada nucleótido que se añade a una nueva cadena de ADN en crecimiento es, en realidad, un nucleósido trifosfato, que
en realidad es un azúcar (desoxirribosa), una base nitrogenada y tres grupos fosfato. A medida que cada monómero se
une al extremo en crecimiento de una cadena de ADN, pierde dos grupos fostato como una molécula de pirofosfato P-
Pi. La hidrólisis posterior del pirofosfato a dos moléculas de Pi es la reacción exergónica que impulsa la polimerización.
3.- Elongación antiparalela:
Los dos extremos de una cadena de ADN son diferentes. Además las dos cadenas de ADN en una doble hélice son
antiparalelas, lo que significa que se orientan en direcciones sopuestas una de otra, por lo que es evidente que las dos
cadenas nuevas formadas durante la replicación del ADN también deben ser antiparalelas a su cadena molde.
Esta estructura antiparalela afecta la replicación, debido a que las ADNpol agregan nucleótidos solo al extremo 3’ libre
de una cadena en crecimiento. De este modo una cadena nueva solo se puede elongar en dirección 5’→3’.
A lo largo de una cadena molde de ADN la ADNpol δ puede sintetizar una cadena complementaria de forma continua
por medio del alargamiento de la cadena nueva en dirección obligatoria 5’→3’. La ADNpol δ se acomoda simplemente
en la horquilla de replicación sobre la cadena molde y agrega nucleótidos de forma continua a la cadena complementaria
a medida que la horquilla progresa. La cadena de ADN sintetizada por medio de este mecanismo se llama:
“hebra
adelantada”.
Para elongar la otra cadena nueva de ADN en dirección obligada 5’→3’, la ADNpol ε debe actuar a lo largo de la otra
cadena molde en dirección contraria a la horquilla de replicación. La cadena de ADN sintetizada en esta dirección se
denomina: “hebra retrasada”. Esta hebra retrasada se sintetiza en una serie de segmentos. Una vez que la burbuja de
replicación se abre lo suficiente, una molécula de ADNpol III se adhiere al molde de la hebra retrasada y se aleja de la
horquilla de replicación, para sintetizar un segmento corto de ADN. A medida que crece la burbuja se puede elaborar
otro segmento de la hebra retrasada de una maneja similar. Estos segmentos de fibra retrasada de denominan:
Fragmentos de Okazaki.
Otra enzima, la
ADN LIGASA, finalmente uni el esqueleto azúcar fosfato de los fragmentos de Okazaki y forma una cadena
de ADN nueva.
La síntesis de la hebra adelantada y la hebra retrasa se producen de forma simultánea y a la misma velocidad. Se
llama hebra retrasada porque su síntesis se retrasa ligeramente en relación con la síntesis de la hebra adelantada;
cada fragmento nuevo no puede comenzar hasta que se haya expuesto una cantidad suficiente de molde en la
horquilla de replicación.
Elisa Lara. Medicina, UNCO.
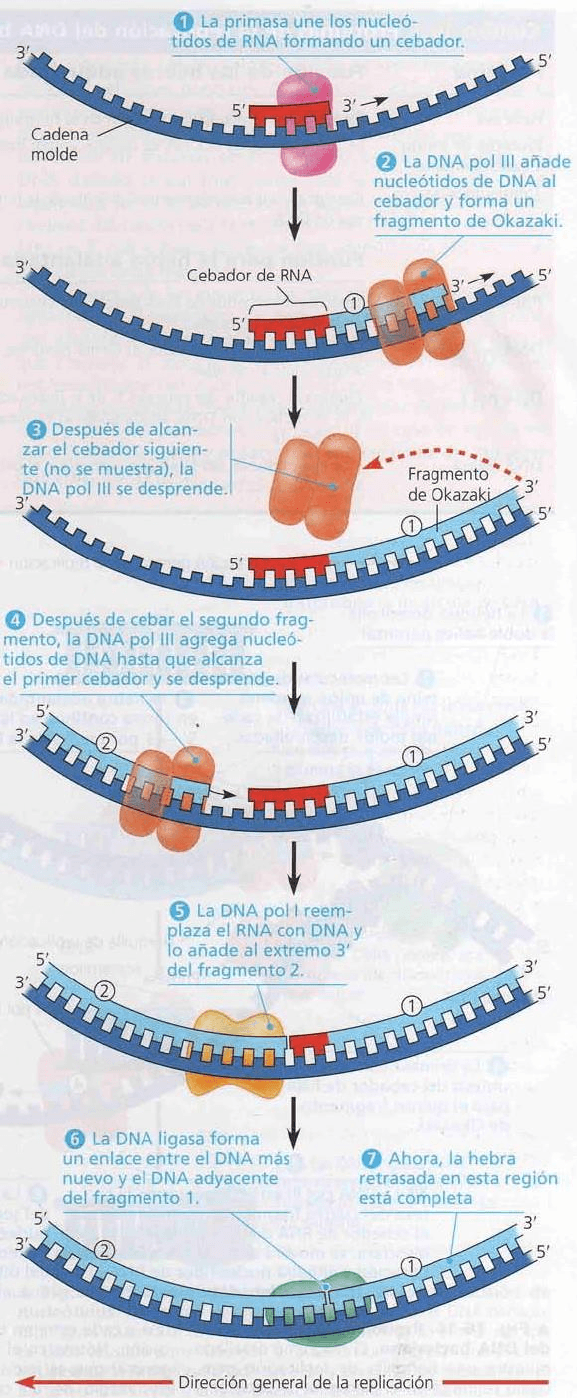
4.- Preparación de la síntesis de ADN.
Las ADN polimerasas no pueden iniciar la síntesis de un
polinucleótido, solo pueden añadir nucleótidos al extremo
3’ de una cadena ya existente que está apareada con las
bases de la cadena molde. La cadena de nucleótidos inicial
es un segmento corto llamado CEBADOR. Los cebadores
pueden estar compuestos de ADN o ARN, pero en el caso
del inicio de la replicación del ADN celular, el cebador es un
segmento corto de ARN con un extremo 3’ disponible. Una
enzima denominada
PRIMASA puede comenzar una
cadena de ARN desde el principio. La primasa une los
nucleótidos de ARN de uno en uno y sintetiza un cebador
complementario a la cadena molde en el lugar donde se
producirá la iniciación de la nueva cadena de ADN (los
cebadores generalmente tienen de 5 a 10 nucleótidos de
largo).
Luego, la
ADNpol δ o ε añade un nucleótido de ADN al
extremo 3’ del cebador de ARN y continúa agregando
nucleótidos a la cadena de ADN en crecimiento de acuerdo
a las reglas del apareamiento de bases. Solo se requiere un
cebador para que la ADNpol δ comience a sintetizar la
cadena adelantada. Para sintetizar la cadena retrasada, sin
embargo, cada fragmento de Okazaki debe cebarse por
separado, y el ADN es sintetizado por la ADNpol ε.
Otra enzima,
la ARNasa H, degrada la hebra de ARN del
híbrido ADN-ARN. Es una exonucleasa en dirección 5’→3’.
Los huecos resultantes son rellenados por la polimerasa δ
y los fragmentos de ADN son unidos mediante la
ADN
LIGASA, generando una hebra tardía intacta.
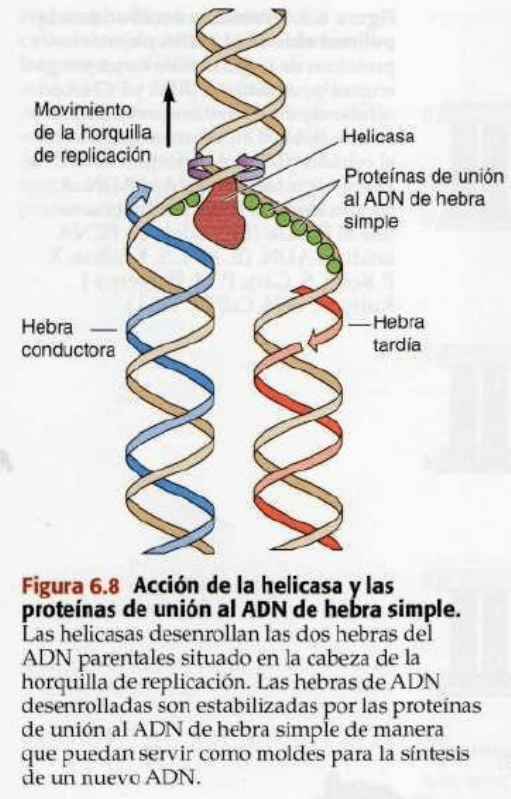
Las
HELICASAS son enzimas que catalizan el
desenrrollamiento del ADN parental, emparejadas con la
hidrólisis del ATP, a la cabeza de la horquilla de replicación.
Las proteínas de unión a cadena simple (factor de
replicación A)
, estabilizan la hebra molde de ADN
desenrrollada manteniéndola en un estado de hebra única
extendida para que sea copiada por las ADNpol δ o ε según
corresponda.
Las TOPOISOMERASAS son enzimas que catalizan la rotura
reversible y la unión de las hebras de ADN. Existen dos tipos
de estas enzimas: La Topoisomerasas I, que rompen solo
una hebra de ADN. Y las Topoisomerasas II que introducen
roturas simultáneas en ambas hebras.
Elisa Lara. Medicina, UNCO.
Estas topoisomerasas sirven como ejes de giro que permiten que a las dos hebras moldes de ADN rotar o pivotar
libremente alrededor de la otra, de manera que la replicación puede continuar sin el enrrollamiento del ADN a la cabeza
de la horquilla de replicación.
Las enzimas implicadas en la replicación del ADN actúan de
forma coordinada para sintetizar las hebras adelantada y
retrasada de ADN simultáneamente en la horquilla de replicación.
Esta tarea se logra a través de la formación de
DÍMEROS DE LAS
POLIMERASAS REPLICATIVAS, acompañadas de subunidades de la
proteína en enganche de carga, la cual se asocia también a una
helicasa en la horquilla de replicación. A continuación, una
molécula de ADNpol δ sintetiza la hebra adelantada, mientras que
la ADNpol ε se ocupa de la hebra retrasada. El molde de la hebra
retrasada se repliega en la horquilla de replicación de tal modo
que la subunidad de la polimerasa encargada de su síntesis avanza
en la misma dirección que la otra subunidad que fabrica la hebra
conductora. La polimerasa que participa en la síntesis de la hebra
tardía se separa de la hebra de ADN al llegar al final de un
fragmento de Okazaki. Continúa asociada la proteína de carga, por
lo que se puede unir de nuevo con gran eficiencia a una nueva
proteína de enganche de deslizamiento en la intersección del
cebador y el molde para comenzar a sintetizar otro fragmento de
Okazaki.
TELOMEROS Y TELOMERASA:
Debido a que las ADNpol solo extienden los cebadores en sentido 5’→3’, son incapaces de copiar los extremos
5’ de las moléculas lineales de ADN. Debido a esto se requieren mecanismos especiales para replicar las
secuencias terminales de los cromosomas lineales.
Estas secuencias, TELÓMEROS, se componen de repeticiones en tándem de secuencias simples de ADN.
Son replicados por la acción de la enzima TELOMERASA, que es capaz de mantener los telómeros catalizando su
síntesis en ausencia de una hebra molde de ADN.
La telomerasa es una TRANSCRIPTASA INVERSA, que SINTETIZA ADN A PARTIR DE ARN. La enzima aporta ella
misma el molde de ARN para la síntesis de ADN.Este molde permite a la telomerasa generar múltiples copias, es
decir, secuencias en tándem, manteniendo los telómeros en ausencia de ADN.
Los defectos en la telomerasa y el mantenimiento normal de los telómeros se asocian con diversas patologías.
Los telómeros se acortan naturalmente medida que envejecen, mandando señales a la célula respecto a su
capacidad restante para dividirse y finalmente, la muerte o la senescencia. El envejecimiento prematuro se
asocia a una alta tasa de pérdida telomérica, y las células cancerosas, de manera opuesta, expresan
anormalmente niveles muy altos de telomerasa, lo que les permite continuar dividiéndose indefinidamente.
2 ESTRUCTURA Y CONFORMACIÓN DEL ADN.pdf
 Estamos procesando este archivo...
Estamos procesando este archivo...
 Lamentablemente la previsualización de este archivo no está disponible. De todas maneras puedes descargarlo y ver si te es útil.
Lamentablemente la previsualización de este archivo no está disponible. De todas maneras puedes descargarlo y ver si te es útil.
Descargar
 Estamos procesando este archivo...
Estamos procesando este archivo...
 Lamentablemente la previsualización de este archivo no está disponible. De todas maneras puedes descargarlo y ver si te es útil.
Lamentablemente la previsualización de este archivo no está disponible. De todas maneras puedes descargarlo y ver si te es útil.